Ressource parisienne en bioinformatique structurale (RPBS)
Modélisation de protéines, de peptides et de leurs interactions, criblage in silico et développement de composés à visée thérapeutique.
Ressource parisienne en bioinformatique structurale (RPBS)
Modélisation de protéines, de peptides et de leurs interactions, criblage in silico et développement de composés à visée thérapeutique.
Ressource parisienne en bioinformatique structurale (RPBS)
La plateforme RPBS développe et met à disposition de la communauté scientifique des méthodes et des outils innovants pour la modélisation moléculaire. Elle combine une activité de recherche propre, incluant la prédiction de structure des peptides et protéines, le docking moléculaire et la dynamique moléculaire, avec une mission de soutien à la recherche académique et industrielle.
La plateforme propose une infrastructure de calcul haute performance équipée de serveurs GPU, un portail intégrant plusieurs dizaines d’outils spécialisés, une capacité d'hébergement de services tiers, ainsi qu’une expertise scientifique en bioinformatique structurale et chémoinformatique. Son accompagnement couvre l’ensemble du cycle des projets : soutien exploratoire pour les études préliminaires en amont de demandes de financement, collaboration scientifique et fourniture de prestations de service.
Membre de l’infrastructure française de bioinformatique (IFB) et de ChemBioFrance, la plateforme RPBS s’inscrit dans les réseaux nationaux et européens de bioinformatique. Elle héberge également le projet iPOP-UP au sein de l’Université Paris Cité.
Expertises et services
- Développement et mise à disposition de services de bioinformatique structurale,
- Mise à disposition d'une infrastructure de calcul haute performance HPC/GPU,
- Accompagnement de projets sous la forme de soutien, de collaboration ou de prestation,
- Modélisation de structure 3D de protéines et peptides,
- Modélisation de complexes protéine-protéine, protéine-peptide et anticorps-antigène,
- Design de peptides interférents,
- Criblage virtuel et docking de petites molécules sur cibles protéiques,
- Filtrage ADME-Tox de chimiothèques,
- Simulation de dynamiques moléculaires et analyse de trajectoires,
- Détection et analyse de poches et de sites de liaison,
- Recherche de similarités structurales et analyse de surfaces protéiques,
- Cartographie d'épitopes par Pepscan, synthèse peptidique sur membrane ou immunoarray,
- Formation et conseil en bioinformatique structurale.
Moyens et équipements
- 42 serveurs CPU totalisant 1 652 curs, 3 192 threads et 9,5 To de RAM, dont un nud bigmem de 1,5 To de RAM,
- 18 serveurs GPU avec 33 cartes, dont 4 NVIDIA A100 80 Go, 3 RTX A6000, 6 Quadro RTX 6000, 6 Tesla A30, 2 RTX 5000 Ada, et des cartes complémentaires RTX 3080 Ti, 3090 et 2080 Ti,
- 2 serveurs de stockage mutualisé d’environ 340 To, dont 125 To de stockage chaud et 215 To de stockage froid, répliqués sur site distant,
- 6 serveurs de virtualisation pour l'hébergement de services tiers (PaaS),
- Serveur dédié MMseqs2 pour la recherche de séquences homologues,
- Environnement Open OnDemand incluant JupyterLab, RStudio, VS Code et HiGlass,
- 2 onduleurs de 30 kVA pour la tolérance aux pannes électriques,
- Portail web intégrant plusieurs dizaines d'outils de bioinformatique structurale.

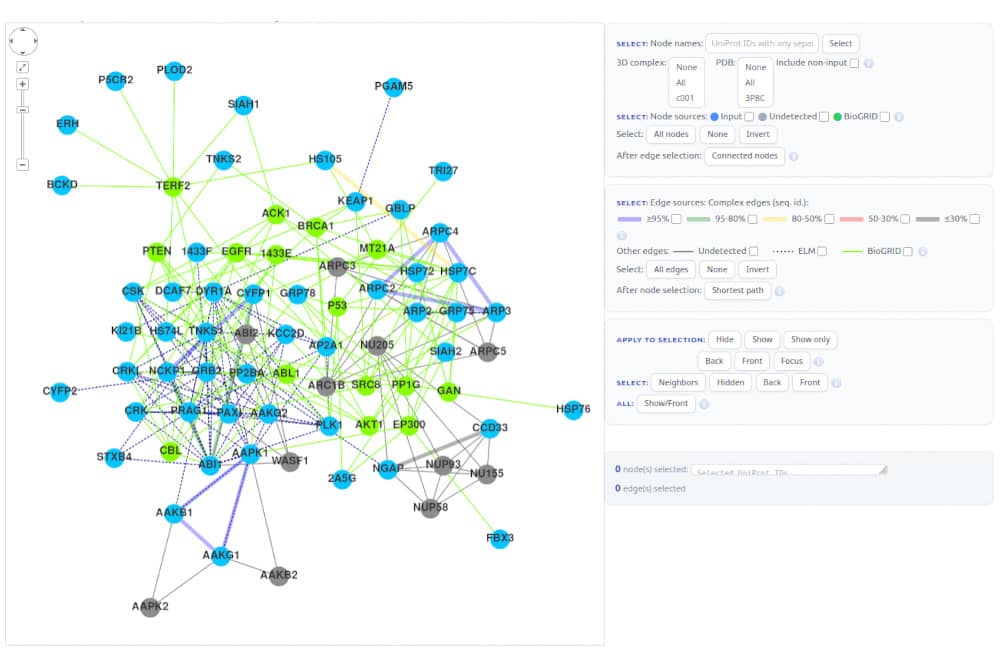
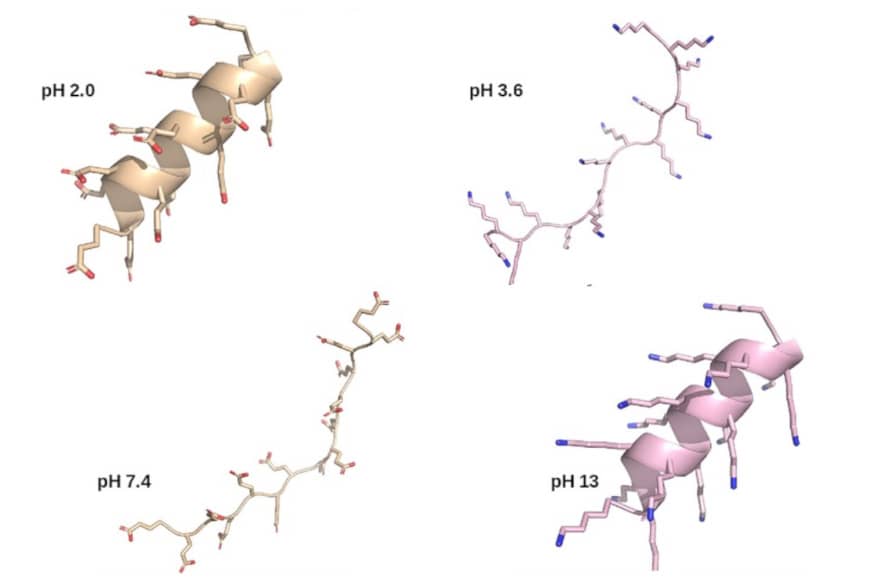
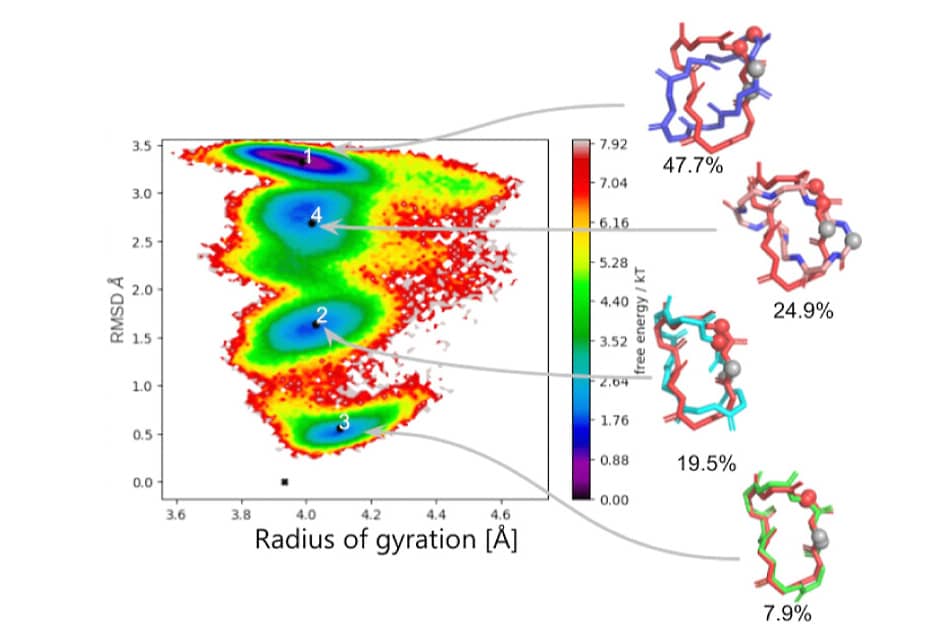
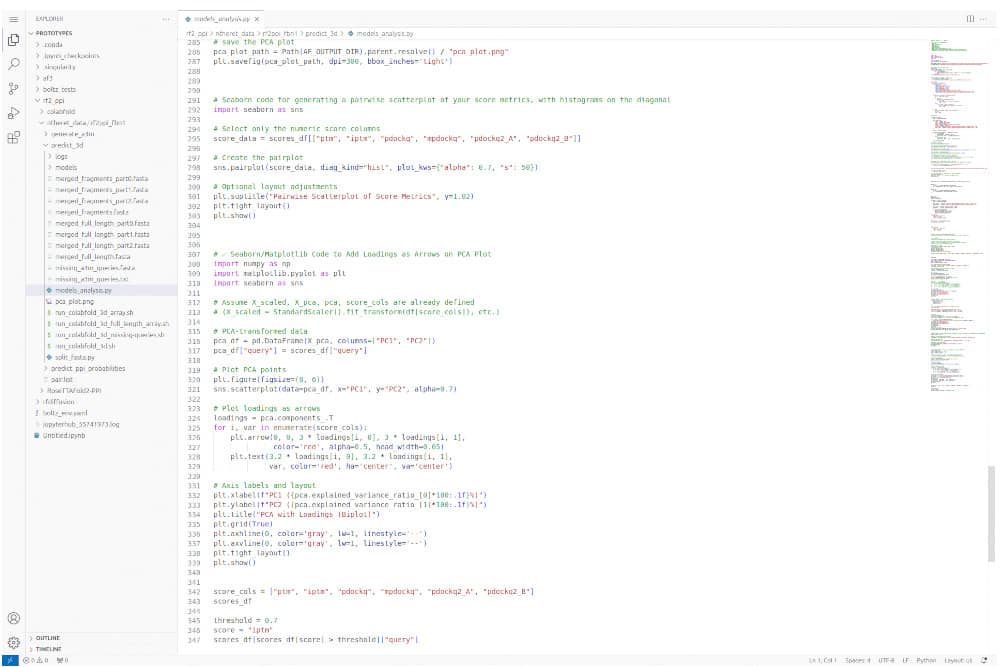

Comment soumettre un projet ?
Pour soumettre un projet à la plateforme RPBS, vous pouvez envoyer un mail à l’adresse rpbs@rpbs.univ-paris-diderot.fr, en décrivant votre problématique et vos attentes. Une première analyse sera réalisée afin d’évaluer la faisabilité technique et scientifique du projet, et d’identifier les ressources à mobiliser en termes d’expertise, de calcul et d’outils.
L’accompagnement de la plateforme peut prendre la forme d’un soutien exploratoire en amont du projet, d’une collaboration scientifique ou, le cas échéant, d’une prestation de service formalisée par un devis et une convention. Les délais de réponse sont généralement de quelques jours pour une première évaluation. La durée de réalisation des expériences dépend de la nature du projet. Elle peut aller de quelques heures pour un support technique à plusieurs semaines ou mois pour une expertise scientifique approfondie incluant un rapport détaillé.
Exemple de projet
Mise au point d’un outil de docking protéine-protéine
L’institut de biologie intégrative de la cellule (I2BC) a sollicité la plateforme RPBS pour codévelopper et déployer un outil de docking protéine-protéine. L'enjeu était de permettre aux biologistes de modéliser l'assemblage de complexes protéiques en exploitant les signaux d'évolution ; un défi majeur pour la compréhension des mécanismes moléculaires du vivant.
La plateforme a mobilisé son expertise en développement logiciel et en bioinformatique structurale pour contribuer à la conception de l’outil InterEvDock3. Celui-ci intègre des signaux co-évolutifs ainsi qu’un scoring au niveau atomique pour sélectionner les modèles les plus fiables. La plateforme a ensuite assuré le déploiement de l’outil sur son portail web, garantissant un accès gratuit et pérenne à la communauté scientifique. Ce travail, qui a abouti à une publication, illustre la capacité de la plateforme à conjuguer recherche méthodologique collaborative et mission de service, de la conception d'un outil jusqu'à sa diffusion auprès de la communauté.
Pour en savoir plus : Quignot C. et al. (2021). InterEvDock3: a combined template-based and free docking server with increased performance through explicit modeling of complex homologs and integration of covariation-based contact. Nucleic Acids Research, 49(W1):277-284.
Contact
RPBS
Bâtiment Lamarck A
5e étage, bureau 515
35 rue Hélène Brion
75205 Paris
Région : Île-de-France +33 (0)1 57 27 84 35
+33 (0)1 57 27 84 35
rpbs@rpbs.univ-paris-diderot.fr
Site de la plateforme
THÉMATIQUES : Bioinformatique, bases de données, Biologie structurale, biophysique, biochimie, Criblage, chimiothèque, chemobiologie
RESPONSABLES SCIENTIFIQUES :
Nicolas Chevrollier
RESPONSABLES TECHNIQUES :
Julien Rey
TUTELLES : Inserm, Université Paris Cité
INFRASTRUCTURES NATIONALES : ChemBioFrance, IFB
LABELLISATION IBiSA : 2025
MOTS CLÉS : Bioinformatique structurale, Modélisation moléculaire, Prédiction de structure, Protéines, Peptides, Docking moléculaire, Criblage virtuel, Drug design, AlphaFold, Dynamique moléculaire, Interactions protéine-protéine, Interactions protéine-ligand, ADME-Tox, Chémoinformatique, Calcul haute performance, GPU, Pepscan, Epitopes
Fiche mise à jour en 2026










